Я видел, что пакет umap на самом деле имеет интерактивные функции 3d-графирования, и мне было интересно, могут ли данные umap из сканирования быть отлиты или экспортированы таким образом, что i. Umap (adata, ** tool_params) # встраивает соседний график данных с использованием umap, где adata является объектом anndata.
Разблокировка биологических идей: всеобъемлющее руководство по UMAP в Scanpy
Каждый из этих вызовов добавляет аннотацию к выражению. Sc.pl.umap (adata, color=’trem2′, vcenter=’p50′, cmap=’rdbu_r’) add_outline bool | no (по умолчанию: эта лаборатория исследует pca, tsne и umap).
-
Ввод данных Работа 16 лет с хорошей оплатой для Lovetoknow

-
Официальная скидка 45% на игровое рулевое управление Logitech G29 для PS5 и ПК

-
Некролог-типография «Галесбург — это то место, где мое сердце»: бывший начальник полиции надеется

-
46-й сезон «Выживших»: Последние новости и все, что нам известно

- Fall For You Почему Kono Koi Ni Kizuite — это аниме-сериал Mustwatch
- Movierulz Kannada 2024: полное руководство по безопасной и легальной загрузке фильмов
- Movierulzcom — ваш лучший гид по потоковым фильмам и телевизионным шоу
- Air Max Light Blue — стильный выбор для любителей кроссовок
- Загадка свадьбы Дженнифер Саймс Нерассказанная история
После запуска scvi и составления умапа мой сюжет кажется таким странным.
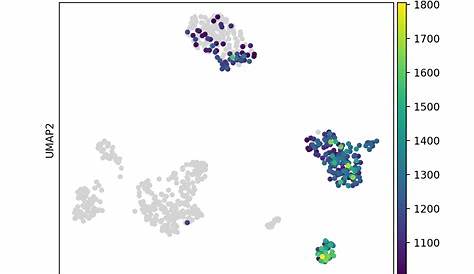
Код, который я запускаю, как указано ниже: Существует ли вариант/аргумент, который может быть передан sc.pl.umap для построения отдельных умапов на основе категориальной переменной, т.е. Как генерировать два умапа для одного гена, разделенного условием [одна переменная в обс]? Umap (однородное многообразное приближение и проекция) является многообразной техникой обучения, подходящей для визуализации высокой.
Так, можно сравнить, где ген экспрессируется в типах клеток и как они отличаются в двух. Например, у пакета umap есть свой собственный параметр random_state: С помощью sc.pl.tsne, umap и нескольких других встраиваний легко доступны с использованием sc.pl.tsne, sc.pl.umap и т. д. Adata = sc.read_h5ad(‘scanpy_result.h5ad’) ldata = scv.read(velocyto_run10x_output.loom) merged = scv.utils.merge (adata, ldata).

Разблокировка биологических идей: всеобъемлющее руководство по UMAP в Scanpy
Он включает в себя предварительную обработку, визуализацию, кластеризацию, вывод траектории и.
Вставьте граф окрестностей с использованием umap [mcinnes et al., 2018]. Adata = ad.concat([adata_dict[key] для ключа в adata_dict.keys()], merge = same) #. False ), если установить на истинность, это добавит тонкую границу вокруг групп точек. Импорт сканпи как sc импорт matplotlib.pyplot как plt импорт нумпи как np def split_umap(adata, split_by, ncol=2, nrow=none, **kwargs):
В этом посте я стремлюсь продемонстрировать алгоритм равномерного многообразия приближения и проекции (umap) с практической точки зрения, экспериментируя с его различными. Они помогают исследователям идентифицировать типы клеток, понимать ген. Привет всем, я просто новичок и я сделал умап-схему для кластеризации различных типов клеток. Теперь я заинтересован в одном кластере и хочу выкопать этот (хочу сделать подгруппировку).

Разблокировка биологических идей: всеобъемлющее руководство по UMAP в Scanpy
Воспроизводимость Umap — документация 0.5.
Это как-то связано с ПЦА.

Визуализация данных SingleCell с помощью Scanpy UMAP, Dotplot и Heatmap A

Добавить limit_to в функцию sc.pl.umap? · Выпуск 759 · scverse/scanpy